Karas eta Hillenkamp eta Tanakaren taldeak, 1980ko hamarkadan garatu zuten Matrix Assisted Laser Desorption Ionization Time of Flight Mass Spectrometry (MALDI/TOF-MS) edo matrizez lagundutako laserraren bidezko desortzio-ionizazioa/hegaldi-denbora masa-espektrometria.

Teknika hau hainbat arlotan erabili da, hain zuzen ere proteinak, peptidoak, lipidoak eta farmakoak identifikatzeko edo polimeroak karakterizatzeko. Beste teknika analitiko batzuekin alderatuz, masa-espektrometriak informazio gehigarria ematen du, analito osoaren eta bere zatien masa molekularrak, esate baterako. Gainera, analisia egiteko laginaren oso kantitate txikia kontsumitzen da (mikrolitroak), denbora laburrean, eta lortzen diren masa molekularrak molekulen egiturarekiko independenteak dira.
Lan honetan, teknika honen oinarriak eta aplikazioak azaltzen eta aztertzen dira. Lehendabizi, ionizazioaren prozesua azalduko da eta ondoren, laginaren prestakuntza. Gero, masa-espektrometroaren atal guztien zereginak ikusiko dira (analizagailuak eta detektagailuak), eta ostean erakusten da zertan datzan Imaging Mass Spectrometry (IMS) edo masa-espektrometriaren bidezko irudia izeneko teknika.
Laburbilduz, teknika honetan, lagina matrizearekin nahasten da eta espektrometroko laserrak laginean dauden osagai guztiak ionizatu egiten ditu. Ondoren, ioien masak analizagailuan banatzen dira eta azkenik, ioiak detektagailura iristen dira eta espektro bat lortzen da. Laginean dagoen konposatu bakoitza, espektroan gailur bezala ikusiko da.
MALDI teknikan, urrats garrantzitsua da aztergai dugun laginetik ioiak sortzea. Orokorrean, laserraren irradiazioa analito molekulen desortzioa eta/edo ionizazioa eragiteko erabiltzen da; matrizea, aldiz, energia absortziorako bitartekari gisa erabiltzen da (1. irudia). Matrizearen aukera erabakigarria da MALDI MS analisirako. Matrize ezberdin asko eta haiek prestatzeko teknika ugari azaltzen dira bibliografian. Oinarri orokorren arabera, arau batzuk eman ahal dira matrizearen aukera egokia, eta horrela, lana sinplifikatzeko. Analitoaren azidotasun edo basikotasunari begiratuz, protoiarekiko afinitate edo gas fasearen basikotasun egokia duten matrizeak aukeratu daitezke.
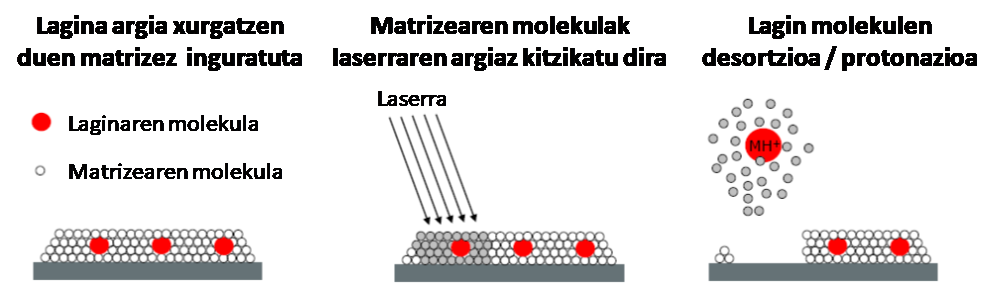
Bestalde, egun, autorradiografia teknika erabili behar da ehun batean lipidoek edo farmakoek duten banaketa ezagutzeko, hau da, arriskutsuak diren isotopo erradioaktiboak erabili behar dira. MALDI Imaging Mass Spectrometry (IMS) edo masa-espektrometriaren bidezko irudiak izeneko teknikari esker, inolako isotopo erradioaktiborik erabili gabe lor daitezke irudiak. Teknika hau, beraz, oso garbia da. IMS teknika, teknika bikaina da ehun biologikoetan dauden molekulen banaketa aztertzeko. Izan ere, molekula mota ezberdinen identifikazioa eta kokapena ahalbidetzen du, konposatuaren edota familia kimikoaren aukera egin aurretik. MALDI IMS egiteko lehendabizi, matrizez estali behar da analizatu nahi den azalera. Matrizez ehunak estaltzeko zenbait teknika erabili dira: lainoztatzea sublimazioa, aerografoa, inprimatzailea… Guztiek dute helburu modura matrizez asetutako disoluzio bat erabilita analizatu nahi den azalera homogeneoki estaltzea. Egun, zenbait enpresak matrizez estaltzeko tresnak garatu dituzte.
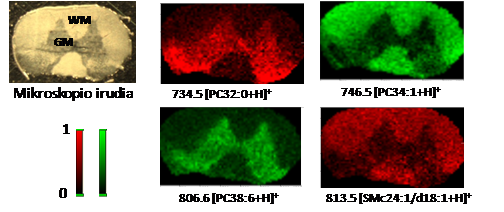
3. irudian, ikus daitezke MALDI IMS bidez lortutako arratoien bizkarrezur-muineko lipido batzuen distribuzioen irudiak. Goiko aldean, ezkerraldean, ehun horren mikroskopio irudia erakusten da, materia grisa eta zuria ondo bereizita. Ondoko irudiak, IMS teknika erabilita lortu dira. Koloreen eskala alboan adierazten da, hots, kolore bizia dagoen lekuan (gorriz edo berdez), espeziearen gailurra intentsitate handikoa da, eta kolorea iluna bada (beltzez), espezie hori ez da izango inguru horretan. Ikusten den bezala, materia zurian (WM) barreiatuta daude PC34:1 (fosfatidilkolina), edo SMc24:1/d18:1 (esfingomielina) bezalako espezie batzuk. Materia grisean (GM) daude PC32:0 eta PC38:6 fosfatidilkolinak bezalako beste batzuk.
- Aldizkaria: Ekaia
- Zenbakia: Ekaia 32
- Artikuluaren izena: MALDI-TOF masa-espektrometria ezagutzen
- Laburpena: Gaur egun, nahiko informazio ageria ematen dute biomolekulak eta materialak karakterizatzeko erabiltzen diren laborategi-teknika analitikoek, baina azaldu ezin diren efektuak edo emaitzak lortzen dira askotan. Horregatik, informazio hau lortzeko, hau da, molekulen mikroegiturak karakterizatzeko edota gertatu diren kutsadurak ezagutzeko ere, gero eta gehiago hedatzen ari da teknika bat, Matrix Assisted Laser Desorption-Ionization/Time of Flight Mass Spectrometry (MALDI/TOF-MS) izenekoa, edo laserraren bidezko desortzio-ionizazio matrizez lagundua/hegaldi-denbora masa-espektrometria teknika. Masa-espektrometria delako karakterizazio teknika hau hainbat alorretara hedatu da, masa molarra jakitea ahalbidetzen duelako inolako zatiketarik gabe eta, aldi berean, ehun edo material baten banaketaren berri ematen duelako Imaging Mass Spectrometry (IMS) edo masa-espektrometriaren bidezko irudia deritzon teknikari esker. Lan honek helburu hartuko du teknika berri honen oinarriak eta aplikazioak azaltzea eta aztertzea.
- Egileak: Antonio Veloso
- Argitaletxea: UPV/EHUko argitalpen zerbitzua
- ISSN: 0214-9001
- Orrialdeak: 83-96
- DOI: 10.1387/ekaia.16965
Egileez: Antonio Veloso Polymaten eta UPV/EHUn dabil.
Ekaia aldizkariarekin lankidetzan egindako atala.

1 iruzkina
[…] Elektro-spray bidezko ionizazioa eta Matrizeak lagundutako Laser-Desortzioa/ionizazioa (ingelesez, MALDI). Horrela, hegoak jarri zitzaizkien “molekula elefanteei”. Hala esan zuen John B. Fennek […]